估计阅读时长: 10 分钟https://github.com/xieguigang/sciBASIC 根据积分表达式,微分方程的数值解关键在于微分方程的初值及计算微分方程式在tm(上一时刻)与tm+d(下一时刻)与坐标轴围成面积,若这个面积计算得越准确则得到的数值解也就越精确。微分表达式中与坐标轴围成的面积可表示如下,在实施算法的时候可以结合这个图更加直观点: 从上面的示意图可以看出,一段需要进行面积积分的曲线实际上是由多个梯形构成的多边形。那我们实际上只需要将这些梯形的面积都求出来,然后加起来就好了。 这里的梯形分割就是一种欧拉逼近的思想,欧拉逼近的几何意义,就是我们可以使用一段折线来近似的逼近一条曲线。 利用欧拉逼近,我们可以将一个精确的微分方程曲线 近似的使用线段来表示 Order by Date Name Attachments ODE_Trapezoidal • 30 kB • […]
估计阅读时长: 8 分钟https://github.com/rsharp-lang/R-sharp R#语言的语法主要来自于R语言,其在保留了很多的R语言特性的同时,也添加了很多新语法特性。对于R#与R语言之间相同的语法特性,在本简明教程中我就不再叙述了,在这里主要是给大家说明一下R#语言相对于R语言新增的一些语法特性。 R#语言中的向量 R#语言任然保持着和其前辈R语言一样的向量化编程的特性。对于声明一个向量,在R语言之中,需要使用c函数进行申明,而对于R#语言而言,除了使用c函数,还可以直接使用方括号进行申明,例如: x = c("A","B","C") # x # [1] "A" "B" "C" x = […]
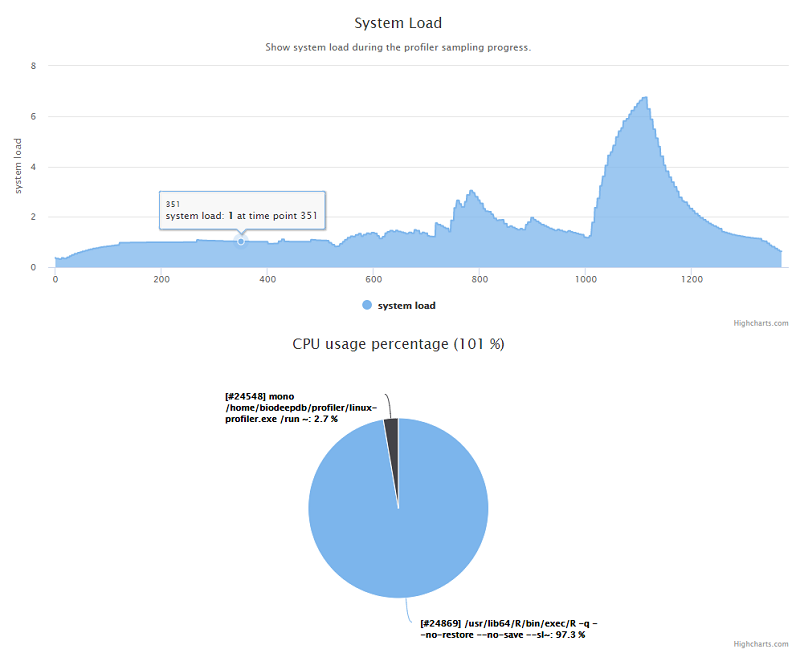
估计阅读时长: 6 分钟https://github.com/xieguigang/linux-profiler 废话不多说,首先给出一个 demo报告链接 给大家看看这个小工具的成品输出。 在去年的工作中,因为公司需要购买新的服务器做集群计算,需要一个工具来记录之前的服务器在数据分析上的性能瓶颈。于是花了两天的时间赶出来了这个专门应用于Linux系统的性能记录工具。这个小工具是一个开源项目,大家可以在Github上阅读这个开源项目(linux-profiler)的源代码。 Order by Date Name Attachments systemLoad • 53 kB • 828 […]
估计阅读时长: 4 分钟https://github.com/xieguigang/bclusterTree 对于二叉树,大家肯定不会陌生。二叉树其实就是一个有向无环图(有向:访问的方向是从父节点指向子节点;无环:子节点不会成为其父辈节点的父节点),大家可以从根节点一直往下访问到任意一个叶节点;节点间的方向是根据键值的比较的大小结果来建立的,大的值在右边,小的值在左边(《左迁与右迁》),零值在当前节点。 二叉树示意图来自于这篇博文《Self-balanced Binary Search Trees with AVL in JavaScript》 Order by Date Name Attachments Rplot […]
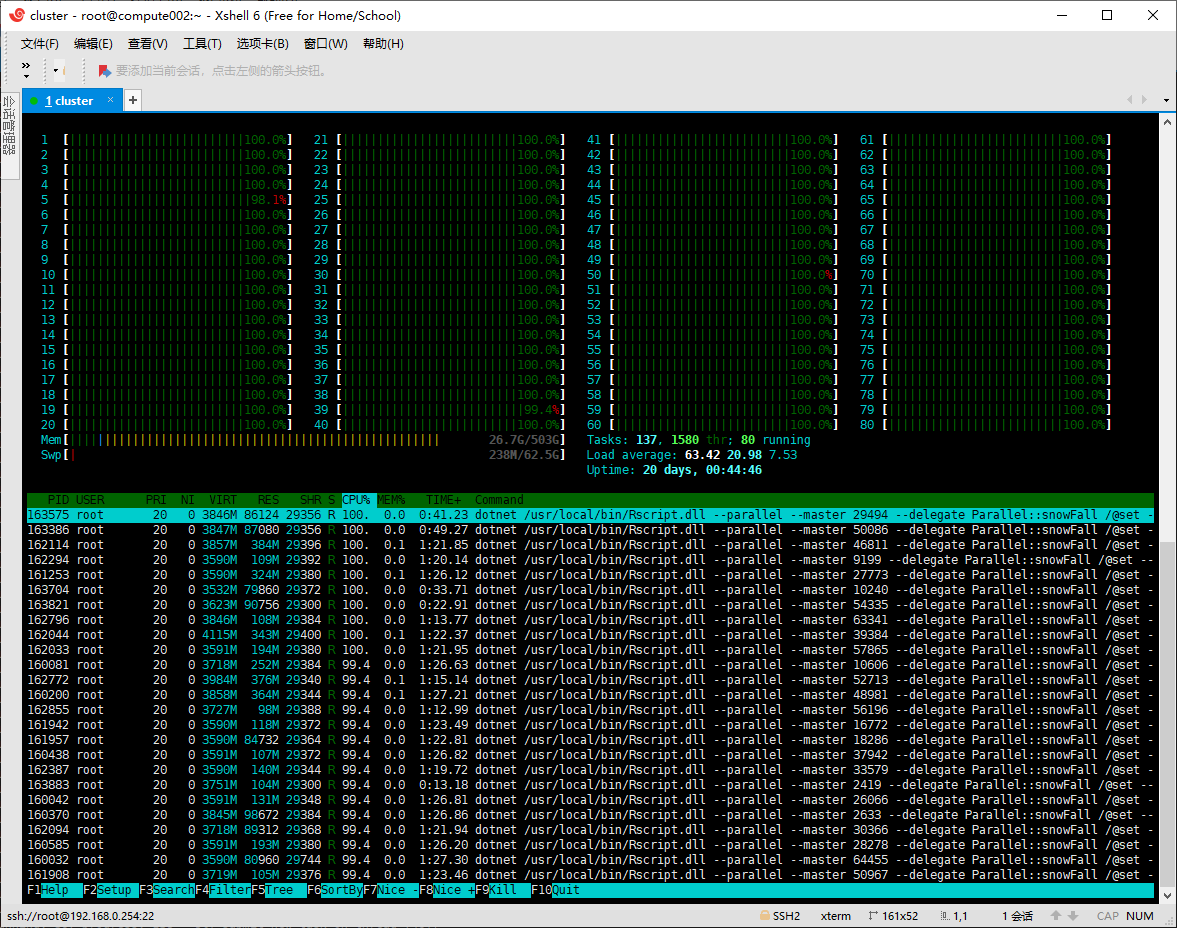
估计阅读时长: 5 分钟https://github.com/xieguigang/Darwinism 最近在做一个代谢组学的数据分析程序,由于需要被分析的质谱原始数据的计算量非常大,所以肯定会需要上并行计算。在并行计算中,分为两种模式:线程并行以及进程并行。 关于如果选择脚本代码的并行模式,我在这里借用了matlab文档网站里面的一张图来给大家做参考: 《Choose Between Thread-Based and Process-Based Environments》 Order by Date Name Attachments super_computing • […]
估计阅读时长: 3 分钟在BILIBILI上观看视频:《【GCModeller教程】基因组GO功能注释原理》 哈喽,各位小伙伴们好啊,你们可爱的六神无主鸠今天又开新课了。今天主要为大家讲解的内容是GO基因功能注释的原理和操作。在开始今天的新视频前,我先为大家来讲一个圣经中的神话: 大洪水过去后, 诺亚的三个儿子的后裔形成了人类的三大支系,居住在世界各地,遍布地面。那时候人们的语言、口音都没有分别。他们在往东边迁移的时候,在示拿这个地方遇见一片平原,就在那里住下。因为在平原上,用作建筑的石料很不易得到,他们就发明了制造砖的方法,用泥作成方块,再用火烧透,他们就拿砖当石头,又拿石漆当灰泥,建造起繁华的巴比伦城。 人们为自己的业绩感到骄傲,他们决定在巴比伦修一座通天的高塔,来传颂自己的赫赫威名,并作为集合全天下弟兄的标记,以免分散。因为大家语言相通,同心协力,阶梯式的通天塔修建得非常顺利,很快就高耸入云。 上帝是不允许凡人达到自己的高度的。他看到人们这样统一强大,心想,他们语言都一样,如果真修成宏伟的通天塔,那以后还有什么事干不成呢? 必须制止人类接近自己的狂妄。上帝就离开天国到人间,变乱了人们的语言。人们各自操起不同的语言,感情无法交流,思想很难统一。修造工程因语言纷争而停止了,通天塔的建造终于半途而废了。 Order by Date Name Attachments gene_ontology_annotation • 576 kB […]
估计阅读时长: 2 分钟在BILIBILI上观看视频:《【GCModeller教程】基因组功能富集计算原理》 Order by Date Name Attachments 20190818_GSEA_release.mp4_20190921_225144.467 • 226 kB • 828 click 2021年5月30日Fisher Exact Test […]
估计阅读时长: 2 分钟在BILIBILI上观看视频:《【GCModeller教程】KEGG代谢途径注释原理 (重置版)》 Order by Date Name Attachments kegg_annotation • 468 kB • 925 click 2021年5月30日release.mp4_20190921_225235.396 • […]
估计阅读时长: 2 分钟https://github.com/xieguigang/mzkit 在BILIBILI上观看视频:《【BioNovoGene Mzkit教程】代谢组学原始数据处理基础》 Order by Date Name Attachments profile_videocard • 211 kB • 852 click 2021年5月29日metabolims […]
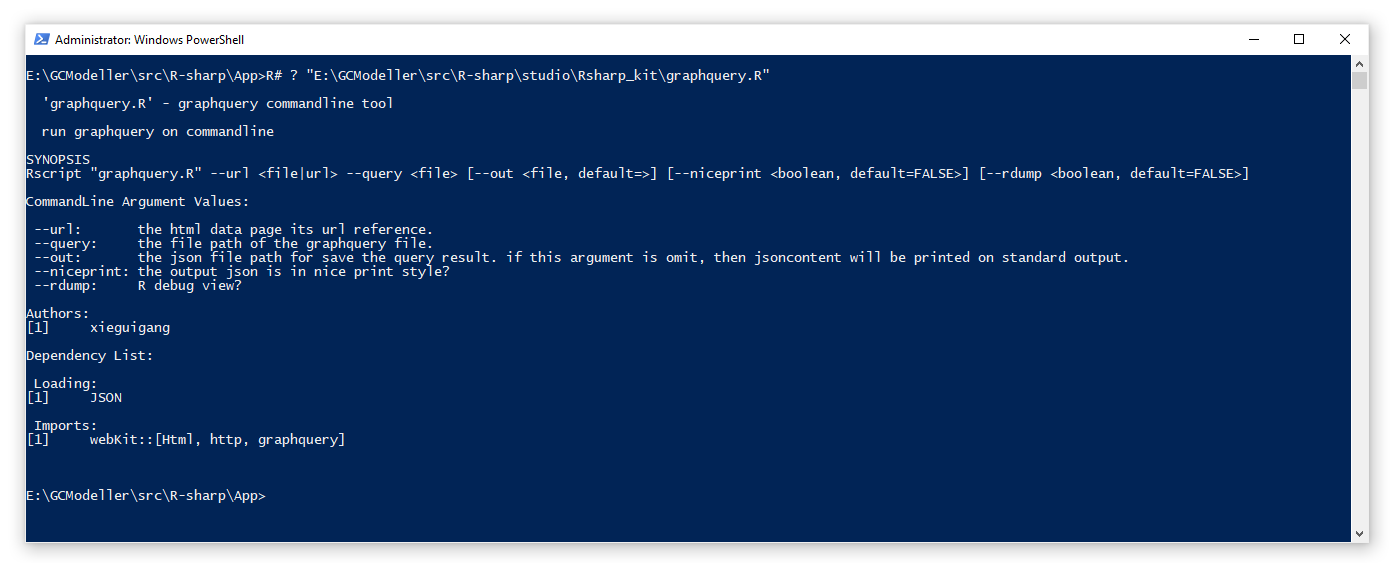
估计阅读时长: 9 分钟前段时间由于工作的需要,会需要从一些网站上抓取数据用来做数据分析。在原来我进行网页爬虫开发的时候,一般会需要专门针对网页格式,使用大量的正则表达式进行内容的解析。由于你也知道,VisualBasic语言所开发的程序为一个编译好的Assembly文件,所以假若所需要爬取的网页格式变化了,我们就需要对代码做修改和重新编译。这个时候就会非常的不方便。 Order by Date Name Attachments ea5d2885-bba5-410f-b02b-0589613412ed • 12 kB • 853 click 2021年5月29日graphquery_Rscript • 36 […]







[…] 我们在基于前面所论述的《通过diamond软件进行blastp搜索》对大规模的基因组数据进行了代谢酶的EC number的注释以及按照文章《基因组功能注释(EC Number)的向量化嵌入》的方法,得到了一个比较大的基因组代谢酶TF-IDF嵌入丰度矩阵后,如果将这里所得到的嵌入结果矩阵中的基因组,基于Family层级的物种分类分组看作为单细胞转录数据中的细胞分群结果,能否基于单细胞数据分析方法来分析和可视化我的基因组功能嵌入的结果矩阵呢? […]
[…] 我们在基于前面所论述的《通过diamond软件进行blastp搜索》对大规模的基因组数据进行了代谢酶的EC number的注释以及按照文章《基因组功能注释(EC Number)的向量化嵌入》的方法,得到了一个比较大的基因组代谢酶TF-IDF嵌入丰度矩阵后,如果将这里所得到的嵌入结果矩阵中的基因组,基于Family层级的物种分类分组看作为单细胞转录数据中的细胞分群结果,能否基于单细胞数据分析方法来分析和可视化我的基因组功能嵌入的结果矩阵呢? […]
[…] 对于基于ec number来生成层级数据,我们直接使用《酶EC编号结构解析》文章末尾所展示的层级数据生成函数来实现。 […]
[…] 在前面的一篇《基因组功能注释(EC Number)的向量化嵌入》博客文章中,针对所注释得到的微生物基因组代谢信息,进行基于TF-IDF的向量化嵌入之后。为了可视化向量化嵌入的效果,通过UMAP进行降维,然后基于降维的结果进行散点图可视化。通过散点图可视化可以发现向量化的嵌入结果可以比较好的将不同物种分类来源的微生物基因组区分开来。 […]
😲啊?