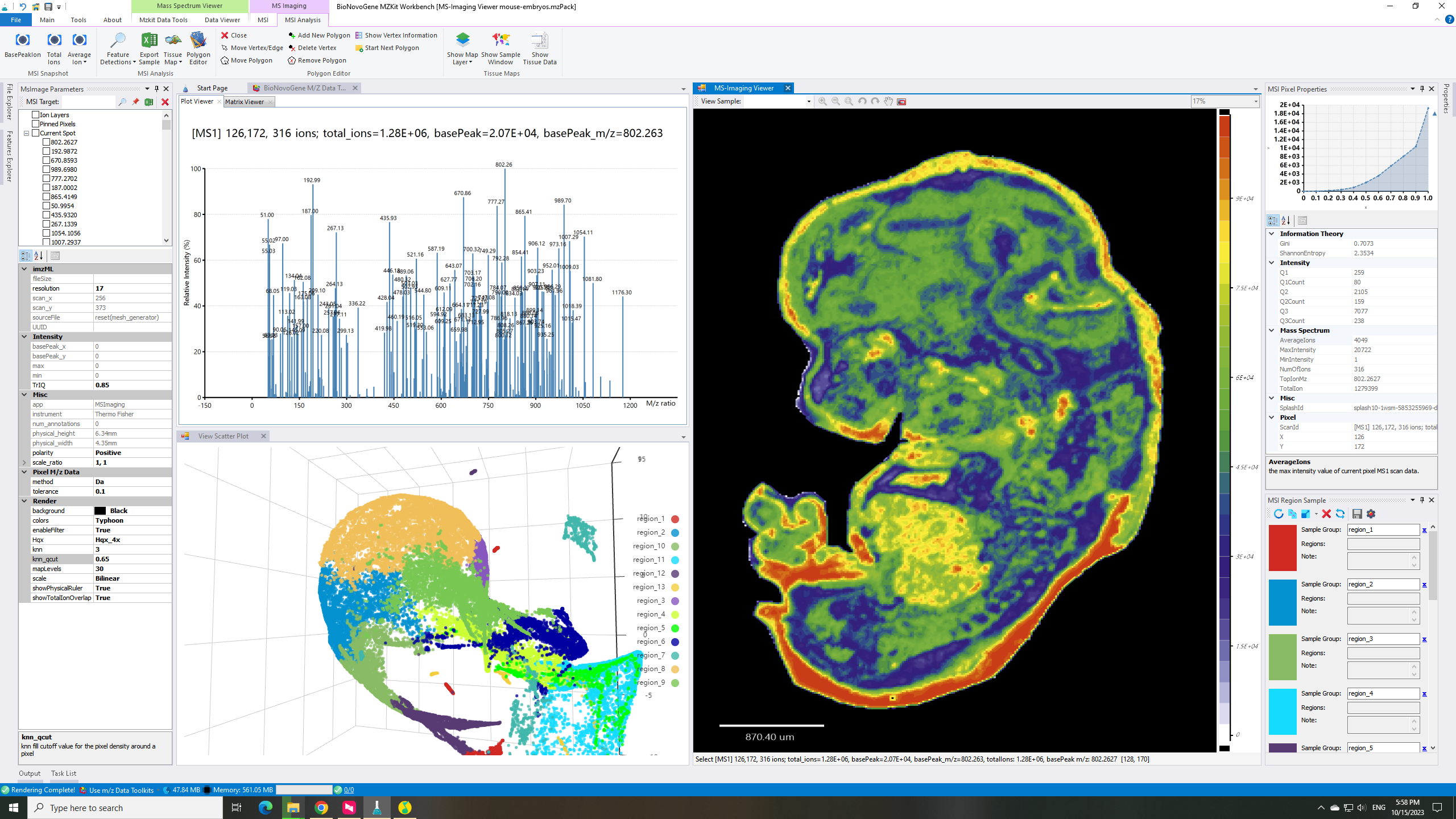
估计阅读时长: 6 分钟大家好呀,今天的这篇文章主要是为了回答在B站上的一位小伙伴的请求 Order by Date Name Attachments render-parameters • 18 kB • 836 click 2023年10月15日view-umap • 427 […]
估计阅读时长: 2 分钟在BILIBILI上观看视频:【空间代谢组学】AP-MALDI 质谱成像技术介绍 哈啰,大家好呀,鸽了大半年之后,你们的小姐姐又回来啦。为了更好的制作出质量更高的视频,你们的六神无主鸠小姐姐呀,在这大半年的时间里面一直在努力的学习新技术。经过半年的钻研学习,收获满满。谈到最近几年的热门尖端技术,大家都会谈论到空间转录组和单细胞技术。一般而言,代谢组学的发展要稍微滞后于转录组学研究。最近一年呢,随着空间转录组的热度的降低,空间代谢组的热潮也终于姗姗来迟终于到来了。今天呢,我想要为大家介绍的是在最近几年内出现的,目前比较火热的空间代谢组学研究领域内的质谱成像技术。 Order by Date Name Attachments 3D-MS-imaging-using-dual-beam-and-dual-spectrometer-mode-10-of-single-rat-alveolar • 99 kB • 1067 click 2022年5月6日Microsoft […]
估计阅读时长: 2 分钟https://github.com/xieguigang/mzkit 在BILIBILI上观看视频:《【BioNovoGene Mzkit教程】代谢组学原始数据处理基础》 Order by Date Name Attachments profile_videocard • 211 kB • 959 click 2021年5月29日metabolims […]



[…] 我们在基于前面所论述的《通过diamond软件进行blastp搜索》对大规模的基因组数据进行了代谢酶的EC number的注释以及按照文章《基因组功能注释(EC Number)的向量化嵌入》的方法,得到了一个比较大的基因组代谢酶TF-IDF嵌入丰度矩阵后,如果将这里所得到的嵌入结果矩阵中的基因组,基于Family层级的物种分类分组看作为单细胞转录数据中的细胞分群结果,能否基于单细胞数据分析方法来分析和可视化我的基因组功能嵌入的结果矩阵呢? […]
[…] 我们在基于前面所论述的《通过diamond软件进行blastp搜索》对大规模的基因组数据进行了代谢酶的EC number的注释以及按照文章《基因组功能注释(EC Number)的向量化嵌入》的方法,得到了一个比较大的基因组代谢酶TF-IDF嵌入丰度矩阵后,如果将这里所得到的嵌入结果矩阵中的基因组,基于Family层级的物种分类分组看作为单细胞转录数据中的细胞分群结果,能否基于单细胞数据分析方法来分析和可视化我的基因组功能嵌入的结果矩阵呢? […]
[…] 对于基于ec number来生成层级数据,我们直接使用《酶EC编号结构解析》文章末尾所展示的层级数据生成函数来实现。 […]
[…] 在前面的一篇《基因组功能注释(EC Number)的向量化嵌入》博客文章中,针对所注释得到的微生物基因组代谢信息,进行基于TF-IDF的向量化嵌入之后。为了可视化向量化嵌入的效果,通过UMAP进行降维,然后基于降维的结果进行散点图可视化。通过散点图可视化可以发现向量化的嵌入结果可以比较好的将不同物种分类来源的微生物基因组区分开来。 […]
😲啊?